Mediator (Koaktivator) - Mediator (coactivator)
Mediator ist ein Proteinkomplex , der als Transkriptions coactivator in allen Eukaryonten . Es wurde 1990 im Labor von Roger D. Kornberg , dem Nobelpreisträger für Chemie 2006, entdeckt . Mediatorkomplexe interagieren mit Transkriptionsfaktoren und RNA-Polymerase II . Die Hauptfunktion von Mediatorkomplexen besteht darin, Signale von den Transkriptionsfaktoren an die Polymerase zu übertragen.
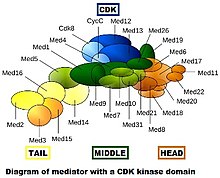
Mediatorkomplexe sind auf evolutionärer, kompositorischer und konformationeller Ebene variabel. Das erste Bild zeigt nur einen "Schnappschuss" dessen, woraus ein bestimmter Mediatorkomplex bestehen könnte, aber es zeigt sicherlich nicht genau die Konformation des Komplexes in vivo . Im Laufe der Evolution ist der Mediator komplexer geworden. Es wird angenommen, dass die Hefe Saccharomyces cerevisiae (ein einfacher Eukaryont ) bis zu 21 Untereinheiten im Kernmediator (ausschließlich des CDK-Moduls) hat, während Säugetiere bis zu 26 haben.
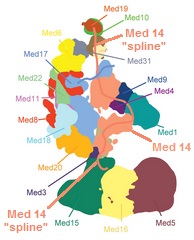
Einzelne Untereinheiten können unter anderen Bedingungen fehlen oder durch andere Untereinheiten ersetzt werden. Außerdem gibt es viele intrinsisch ungeordnete Regionen in Mediatorproteinen, die zur Konformationsflexibilität beitragen können, die sowohl mit als auch ohne andere gebundene Proteine oder Proteinkomplexe beobachtet wird. Ein realistischeres Modell eines Mediatorkomplexes ohne das CDK-Modul ist in der zweiten Abbildung dargestellt.
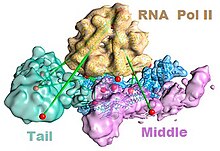
Der Mediatorkomplex wird für die erfolgreiche Transkription durch die RNA-Polymerase II benötigt. Es wurde gezeigt , dass Mediator Kontakte mit der Polymerase im Transkriptions - Präinitiationskomplex herstellt . Ein aktuelles Modell, das die Assoziation der Polymerase mit dem Mediator in Abwesenheit von DNA zeigt, ist in der Abbildung links gezeigt. Neben der RNA-Polymerase II muss der Mediator auch mit Transkriptionsfaktoren und DNA assoziieren. Ein Modell solcher Wechselwirkungen ist in der Abbildung rechts dargestellt. Beachten Sie, dass die unterschiedlichen Morphologien des Mediators nicht unbedingt bedeuten, dass eines der Modelle richtig ist; vielmehr können diese Unterschiede die Flexibilität des Mediators widerspiegeln, wenn er mit anderen Molekülen interagiert. Zum Beispiel erfährt der Mediatorkomplex nach Bindung des Enhancers und des Core-Promotors eine Zusammensetzungsänderung, bei der das Kinasemodul von dem Komplex dissoziiert, um eine Assoziation mit RNA-Polymerase II und eine Transkriptionsaktivierung zu ermöglichen .
Der Mediator-Komplex befindet sich im Zellkern . Es ist für die erfolgreiche Transkription fast aller Klasse-II- Genpromotoren in Hefe erforderlich . Bei Säugetieren funktioniert es auf die gleiche Weise. Der Mediator fungiert als Coaktivator und bindet an die C-terminale Domäne des RNA-Polymerase-II- Holoenzyms und fungiert als Brücke zwischen diesem Enzym und Transkriptionsfaktoren .
Struktur
Der Hefe-Mediator-Komplex ist ungefähr so massiv wie eine kleine Untereinheit eines eukaryontischen Ribosoms . Der Hefe-Mediator besteht aus 25 Untereinheiten, während die Säuger-Mediator-Komplexe etwas größer sind. Mediator kann in 4 Hauptteile unterteilt werden: Kopf, Mitte, Schwanz und das vorübergehend assoziierte CDK8-Kinase-Modul.
Mediator-Untereinheiten haben viele intrinsisch ungeordnete Regionen, die "Splines" genannt werden, die wichtig sein können, um die strukturellen Veränderungen des Mediators zu ermöglichen, die die Funktion des Komplexes verändern. Die Abbildung zeigt, wie die Splines der Med 14-Untereinheit einen großen Teil des Komplexes miteinander verbinden und dennoch Flexibilität ermöglichen.
Es wurden Mediatorkomplexe gefunden oder produziert, denen eine Untereinheit fehlt. Diese kleineren Mediatoren können bei einigen Aktivitäten noch normal funktionieren, aber andere Fähigkeiten haben sie nicht. Dies weist auf eine etwas unabhängige Funktion einiger der Untereinheiten hin, während sie Teil des größeren Komplexes sind.
Ein weiteres Beispiel für strukturelle Variabilität ist bei Vertebraten zu sehen, bei denen sich 3 Paraloge von Untereinheiten des Cyclin- abhängigen Kinasemoduls durch 3 unabhängige Genduplikationsereignisse gefolgt von Sequenzdivergenz entwickelt haben.
Es gibt einen Bericht, dass Mediator stabile Assoziationen mit einer bestimmten Art von nicht-kodierender RNA , ncRNA-a, bildet. Es wurde auch gezeigt , dass diese stabilen Assoziationen die Genexpression in vivo regulieren und durch Mutationen in MED12 verhindert werden , die das FG - Syndrom beim Menschen verursachen . Somit kann die Struktur eines Mediatorkomplexes sowohl durch RNA als auch durch proteinartige Transkriptionsfaktoren erweitert werden.
Funktion
Der Mediator wurde ursprünglich entdeckt, weil er für die Funktion der RNA-Polymerase II wichtig war, aber er hat viel mehr Funktionen als nur Interaktionen an der Transkriptionsstartstelle.
RNA-Polymerase II-Mediator-Kern-Initiationskomplex
Mediator ist eine entscheidende Komponente für die Transkriptionsinitiation. Mediator interagiert mit dem Prä-Initiationskomplex, bestehend aus RNA-Polymerase II und den allgemeinen Transkriptionsfaktoren TFIIB, TFIID, TFIIE, TFIIF und TFIIH, um die Transkription zu stabilisieren und zu initiieren. Studien von Mediator-RNA Pol II-Kontakten in knospender Hefe haben die Bedeutung von TFIIB-Mediator-Kontakten bei der Bildung des Komplexes hervorgehoben. Interaktionen von Mediator mit TFIID im Initiationskomplex wurden gezeigt.
Die Struktur eines Core Mediators (cMed), der mit einem Core-Pre-Initiation-Komplex verbunden ist, wurde aufgeklärt.
RNA-Synthese
Der Präinitiationskomplex, der Mediator, Transkriptionsfaktoren, ein Nukleosom und RNA-Polymerase II enthält, ist wichtig, um die Polymerase für den Transkriptionsstart zu positionieren. Bevor die RNA-Synthese stattfinden kann, muss die Polymerase vom Mediator dissoziieren. Dies scheint durch Phosphorylierung eines Teils der Polymerase durch eine Kinase erreicht zu werden. Wichtig ist, dass Mediator- und Transkriptionsfaktoren nicht von der DNA dissoziieren, wenn die Polymerase mit der Transkription beginnt. Vielmehr verbleibt der Komplex am Promotor, um eine weitere RNA-Polymerase zu rekrutieren, um eine weitere Transkriptionsrunde zu beginnen.
Es gibt einige Hinweise darauf, dass ein Mediator in einer Hefe an der Regulierung von RNA-Polymerase III (Pol III)-Transkripten von tRNAs beteiligt ist. Zur Unterstützung dieser Beweise zeigte ein unabhängiger Bericht eine spezifische Assoziation des Mediators mit Pol III in Saccharomyces cerevisiae . Diese Autoren berichteten auch über spezifische Assoziationen mit RNA-Polymerase I und Proteinen, die an der Transkriptionsverlängerung und RNA-Prozessierung beteiligt sind, was andere Beweise für die Beteiligung des Mediators an der Verlängerung und Prozessierung unterstützt.
Chromatin-Organisation
Der Mediator ist am "Looping" von Chromatin beteiligt , das entfernte Regionen eines Chromosoms in größere physische Nähe bringt. Die oben erwähnte ncRNA-a ist an einem solchen Looping beteiligt. Enhancer-RNAs (eRNAs) können ähnlich funktionieren.
Zusätzlich zum Looping von Euchromatin scheint der Mediator an der Bildung oder Aufrechterhaltung von Heterochromatin an Zentromeren und Telomeren beteiligt zu sein .
Signaltransduktion
Die TGFβ-Signalgebung an der Zellmembran führt zu 2 verschiedenen intrazellulären Signalwegen . Eine davon hängt von MED15 ab, während die andere von MED15 unabhängig ist. In beiden menschlichen Zellen und Caenorhabditis elegans MED15 wird in Lipidhomöostase durch den Stoffwechselweg beteiligt beteiligt SREBPs in der Modellpflanze Arabidopsis thaliana das Ortholog von MED15 wird für die Signalisierung durch das erforderliche Pflanzenhormon Salizylsäure, während MED25 für die Transkriptionsaktivierung von Jasmonat erforderlich ist , und Schattensignalisierungsreaktionen. Zwei Komponenten des CDK-Moduls (MED12 und MED13) sind am Wnt-Signalweg beteiligt MED23 ist am RAS / MAPK/ERK-Signalweg beteiligt Diese verkürzte Übersicht zeigt die Vielseitigkeit einzelner Mediator-Untereinheiten und führt zu der Idee, dass Mediator ein End- Punkt der Signalwege.
Menschliche Krankheit
Die Beteiligung von Mediatoren an verschiedenen menschlichen Krankheiten wurde überprüft. Da die Hemmung einer Interaktion eines krankheitsverursachenden Signalwegs mit einer Mediatoruntereinheit die allgemeine Transkription, die für eine normale Funktion benötigt wird, möglicherweise nicht hemmt, sind Mediatoruntereinheiten attraktive Kandidaten für therapeutische Wirkstoffe.
Interaktionen
Ein Verfahren, das eine sehr sanfte Zelllyse in Hefe anwendet, gefolgt von einer Co- Immunpräzipitation mit einem Antikörper gegen eine Mediator-Untereinheit (Med 17), hat fast alle zuvor berichteten oder vorhergesagten Wechselwirkungen bestätigt und viele zuvor unvermutete spezifische Wechselwirkungen verschiedener Proteine mit Mediatoren aufgedeckt.
MED 1

Eine Erörterung aller Mediator-Untereinheiten würde den Rahmen dieses Artikels sprengen, aber Details einer der Untereinheiten veranschaulichen die Arten von Informationen, die für andere Untereinheiten gesammelt werden können.
Regulierung durch Mikro-RNAs
Mikro-RNAs sind an der Regulation der Expression vieler Proteine beteiligt. Med1 wird von miR-1 angegriffen, das bei der Genregulation bei Krebserkrankungen eine wichtige Rolle spielt. Der Tumorsuppressor miR-137 reguliert auch MED1.
Embryonalentwicklung der Maus
Nullmutanten sterben in einem frühen Gestationsalter (Embryonaltag 11.5). Bei der Untersuchung von hypomorphen Mutanten (die 2 Tage länger überleben können) wurde festgestellt, dass Plazentadefekte primär tödlich waren und dass es auch Defekte in der Herz- und Leberentwicklung gab, aber viele andere Organe waren normal
Mauszellen und -gewebe
Bei Mäusen können bedingte Mutationen erzeugt werden, die zu bestimmten Zeiten nur bestimmte Zellen oder Gewebe betreffen, so dass sich die Maus bis zum Erwachsenenalter entwickeln und der adulte Phänotyp untersucht werden kann. In einem Fall wurde MED1 in Steuern des Zeitablaufs von Ereignissen teilnehmen gefunden Meiose in männlichen Mäusen. Bedingte Mutanten in Keratinozyten zeigen Unterschiede in der Wundheilung der Haut. Es wurde festgestellt, dass eine bedingte Mutante bei Mäusen Zahnepithel in epidermales Epithel umwandelt , was dazu führte, dass Haare in Verbindung mit den Schneidezähnen wuchsen.
Zusammensetzung der Untereinheit
Der Mediator - Komplex ist mindestens zusammengesetzt 31 Untereinheiten in allen Eukaryonten sucht: MED1 , MED4 , MED6 , MED7 , MED8 , MED9 , MED10 , MED11 , MED12 , MED13 , MED13L, MED14 , MED15 , MED16 , MED17 , MED18 , MED19 , MED20 , MED21 , MED22 , MED23 , MED24 , MED25 , MED26 , MED27 , MED28 , MED29 , MED30 , MED31 , CCNC und CDK8 . Es gibt drei pilzspezifische Komponenten, die als Med2 , Med3 und Med5 bezeichnet werden .
Die Untereinheiten bilden mindestens drei strukturell unterschiedliche Untermodule. Der Kopf und die mittleren Module Interact direkt mit RNA - Polymerase II, während des länglichen Schwanz Modul interagiert mit genspezifischen regulatorischen Proteinen . Mediator, der das CDK8-Modul enthält, ist weniger aktiv als Mediator, dem dieses Modul fehlt, um die transkriptionale Aktivierung zu unterstützen .
- Das Kopfmodul enthält: MED6, MED8, MED11, SRB4/MED17, SRB5/MED18, ROX3/MED19, SRB2/MED20 und SRB6/MED22.
- Das mittlere Modul enthält: MED1, MED4, NUT1/MED5, MED7, CSE2/MED9, NUT2/MED10, SRB7/MED21 und SOH1/MED31. CSE2/MED9 interagiert direkt mit MED4.
- Das Heckmodul enthält: MED2, PGD1/MED3, RGR1/MED14, GAL11/MED15 und SIN4/MED16.
- Das Modul CDK8 enthält: MED12, MED13, CCNC und CDK8. Einzelne Präparate des Mediator-Komplexes, denen eine oder mehrere unterschiedliche Untereinheiten fehlen, wurden verschiedentlich als ARC, CRSP, DRIP, PC2, SMCC und TRAP bezeichnet.
Bei anderen Arten
Unten ist ein speziesübergreifender Vergleich der Untereinheiten des Mediatorkomplexes.
| Untereinheit Nr. | Menschliches Gen | C. elegans- Gen | D. melanogaster- Gen | S. cerevisiae- Gen | Sch. pombe- gen |
|---|---|---|---|---|---|
| MED1 | MED1 | Sop3/mdt-1.1, 1.2 | MED1 | MED1 | med1 |
| Med2 | MED2 | ||||
| Med3 | PID1 | ||||
| MED4 | MED4 | MED4 | MED4 | med4 | |
| Med5 | NUT1 | ||||
| MED6 | MED6 | MDT-6 | MED6 | MED6 | med6 |
| MED7 | MED7 | MDT-7/let-49 | MED7 | MED7 | med7 |
| MED8 | MED8 | MDT-8 | MED8 | MED8 | med8 |
| MED9 | MED9 | MED9 | CSE2 | ||
| MED10 | MED10 | MDT-10 | NUT2 | med10 | |
| MED11 | MED11 | MDT-11 | MED11 | MED11 | med11 |
| MED12 | MED12 | MDT-12/dpy-22 | MED12 | SRB8 | srb8 |
| MED12L | MED12L | ||||
| MED13 | MED13 | MDT-13/let-19 | MED13 | SSN2 | srb9 |
| MED14 | MED14 | MDT-14/rgr-1 | MED14 | RGR1 | med14 |
| MED15 | MED15 | mdt-15 | MED15 | GAL11 | YN91_SCHPO |
| MED16 | MED16 | MED16 | SIN4 | ||
| MED17 | MED17 | MDT-17 | MED17 | SRB4 | med17 |
| MED18 | MED18 | MDT-18 | MED18 | SRB5 | med18 |
| MED19 | MED19 | MDT-19 | MED19 | ROX3 | med19 |
| MED20 | MED20 | MDT-20 | MED20 | SRB2 | med20 |
| MED21 | MED21 | MDT-21 | MED21 | SRB7 | med21 |
| MED22 | MED22 | MDT-22 | MED22 | SRB6 | med22 |
| MED23 | MED23 | MDT-23/sur-2 | MED23 | ||
| MED24 | MED24 | MED24 | |||
| MED25 | MED25 | MED25 | |||
| MED26 | MED26 | MED26 | |||
| MED27 | MED27 | MED27 | med27 | ||
| MED28 | MED28 | MED28 | |||
| MED29 | MED29 | MDT-19 | MED29 | ||
| MED30 | MED30 | MED30 | |||
| MED31 | MED31 | MDT-31 | MED31 | SOH1 | med31 |
| CCNC | CCNC | cic-1 | CycC | SSN8 | pch1 |
| CDK8 | CDK8 | cdk-8 | Cdk8 | SSN3 | srb10 |